2022.9.12�NjL�FPHENIX(���݂�ver.��1.20.1)��Enhanced maps -> Polder Maps��pdb��mtz��ǂݍ��݁AOmit selection������(��F chain a and resid 804)�A�K����output prefix�����đ��点����AMaps -> Create a map from map coefficients�ŁAMTZ file�ɐ����polder map�̏o��(XXX_polder_map_coeffs.mtz)�AModel file��pdb��ǂݍ��݁AAtom selection��omit selection�Ɠ������̂��L�����A�K����Output file prefix�����đ��点��BPHENIX�̃f�B���N�g���̒���FFT_XX(job�ԍ�)�Ƃ����t�H���_�̒��́AXXX_polder_map_coeffs_1.ccp4�Ƃ����t�@�C��(2�ł͂Ȃ�)��PyMOL(����2.4.2���g���Ă܂�)�Ƀh���b�O�A���h�h���b�v�Bisomesh�Ƀ`�F�b�N����āAlevel��3-4���炢�ɂ��āAbuffer��2.0, carve�Ƀ`�F�b�N������load����}�b�v��������Ǝv���܂��B
2019.8.19�NjL�F�����ŏЉ�Ă�����@�����APHENIX��polder map��`���������f�R�y�����ǂ��}�������܂��B�ڂ�����official���Љ�y�[�W���_���������ĉ������B
2016.09.29 Fushinobu
�����������K���h�̓d�q���x�}�b�v�͘_���ɂقڕK���ڂ���}�ł��ˁB��ʓI�ɗp�����Ă���ʏ́uFo -Fc�I�~�b�g�}�b�v�v�i���K���h�����f�����珜���ĕ`����σA-weighted (mFo - DFc)exp(iφc) difference map�j�̍����������ł��������܂��B�ȑO�̃o�[�W��������weight���������ĂȂ������̂Łi���݂܂���j���������Ă܂��B
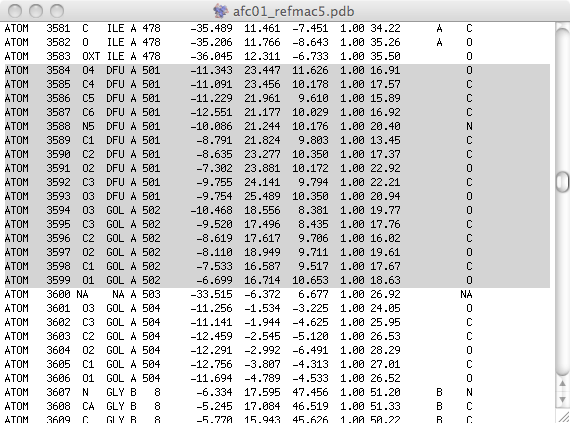
pdb�t�@�C���i��Fafc01_refmac5.pdb�j����\�����������K���h�̍s�������폜���i���̏ꍇ�ADFU A 501��GOL A 502�j�Aafc01_refmac5noLIG.pdb�ȂǂƂ��ĕۑ�����B���F�|���y�v�`�h���̃A�~�m�_�̃}�b�v��\���������ꍇ�ɂ́Aoccupancy�iB-factor�̑O�̐����Œʏ��1.00�ɂȂ��Ă���j���[���ɂ���A�Ƃ������Ƃł�����͂��i���m�F�j

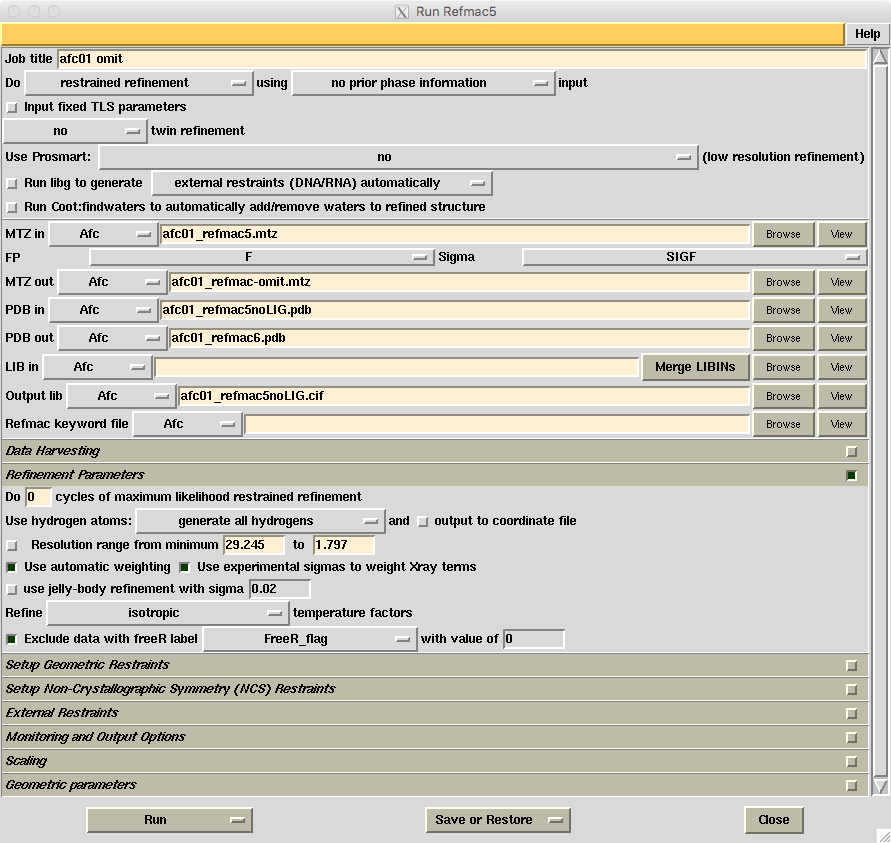
ccp4i�ŁARefinement��Run Refmac 5�BMTZ in�ɍŐV��mtz�t�@�C��(afc01_refmac5.mtz)���APDB in�ɂ����قǍ쐬����pdb�t�@�C��(afc01_refmac5noLIG.pdb)������B�o�͂����mtz�t�@�C��(MTZ out)�ɁAafc01_refmac-omit.mtz�ȂǂƔC�ӂ̖��O������BRefinement Parameters��Do 0 cycles ..�ɂ���B
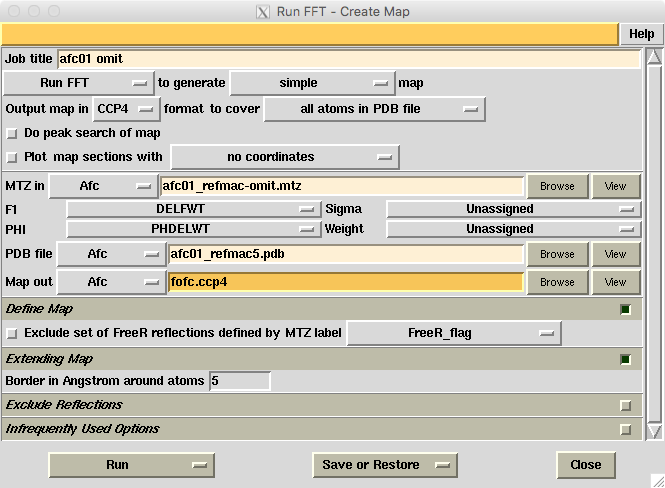
Map & Mask Utilities��Run FFT - Create Map�Bto generate�̃^�u��simple (map)�ŁBto cover��all atoms in PDB file��I�ԁBMTZ in�ɁA��ق�Refmac���o�͂���mtz��I�сAF1��DELFWT���APHI��PHDELWT��I�ԁBPDB file�ɁAnoLIG�ɂ���O��pdb�t�@�C��(afc01_refmac5.pdb)���AMap out�́A***.map�Ƃ��ɂȂ��Ă���Ǝv�����A���������āA�Z�����O�Ŋg���q��ccp4�ɂ���(fofc.ccp4�Ȃ�)�B����͌��PyMol�œǂݍ��ނ��߁BMap out�̏o�͂��f�t�H���g�ł�TEMPORARY�ɂȂ��Ă���Ǝv���̂ŁA���ꂪ�C���Ȃ�K���ȃt�H���_�ɕύX����i�}�ł�ccp4�̍�ƃf�B���N�g��Afc�ɂ��Ă���j
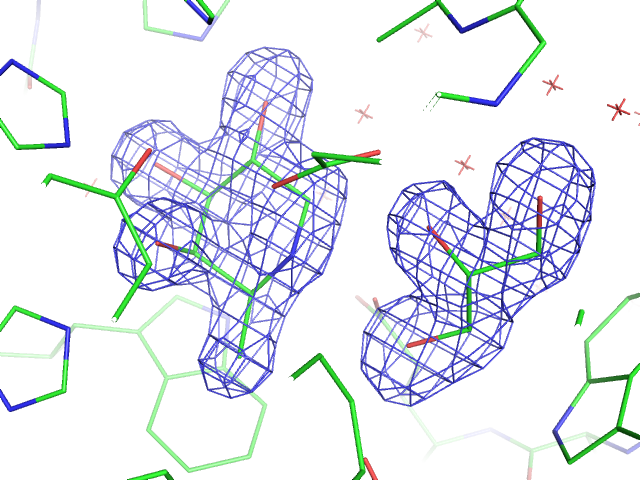
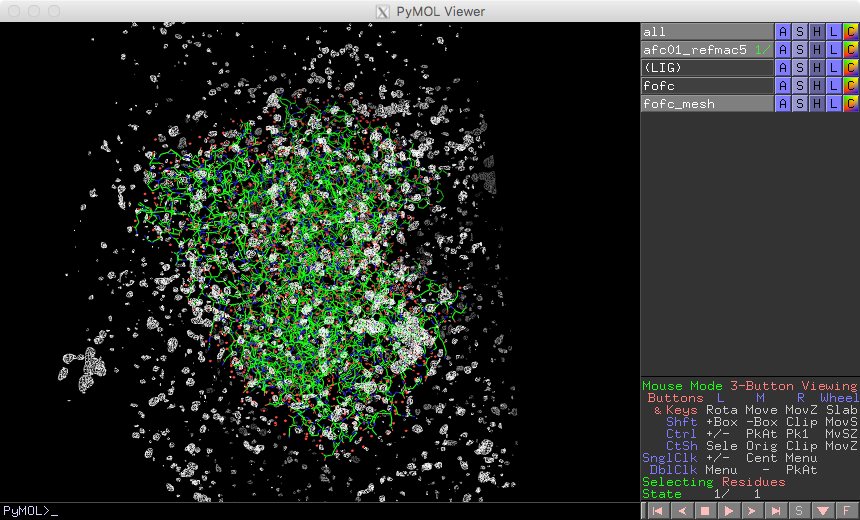
PyMol���N���AnoLIG�ɂ���O��pdb�t�@�C��(afc01_refmac5.pdb)��ǂݍ��ށBFile��Open��fofc.ccp4��ǂݍ��ށB�E�̒���fofc�Ƃ����I�u�W�F�N�g�imap�j�������Bfofc��A�̂Ƃ�����N���b�N��mesh��@ level 3.0�ŁA���b�V���I�u�W�F�N�g(fofc_mesh)�������B
���K���h�i���̏ꍇDFU A 501��GOL A 502�j��select����LIG�Ƃ���selection�����B
>select LIG, (resn DFU and resi 501 and chain A) or (resn GOL and resi 502 and chain A)
�E�̒���(LIG)��A��zoom�œ����BLIG�̎���1.0���i�����q�̎���2.0Å)��4.0σ�̃}�b�v��\������ɂ́A�ȉ��̂悤�ɓ��͂���B
>isomesh fofc_mesh, fofc, 4.0, LIG, 1, 0, 2
mesh�̑�����0.5��0.3���炢��(set mesh_width=0.5)�A�F��tv_blue��olive����������(fofc_mesh�̉E��C��blues��tv_blue)�B���̌�͈ȉ��̂悤�ɂ��ďo�́B
>bg_color white �i�w�i�𔒂ɂ���j
>set ray_shadow=off�@�i�e���f���Ȃ��j
>ray�@�i���C�g���[�X�j
>png fofc�@�ifofc.png�Ƃ����t�@�C���������o���j